Regulation by RNA in Rhizobia
José I. Jiménez Zurdo (IP)
Tenured Scientist CSIC
PHONE NUMBER
+34-958-181-600 ext. 176
Other group members
Research lines
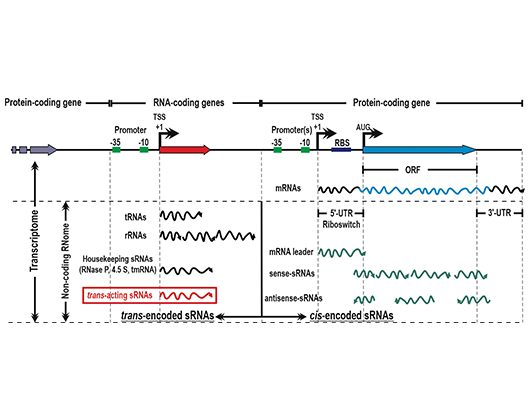
- Rhizobial non-coding transcriptome
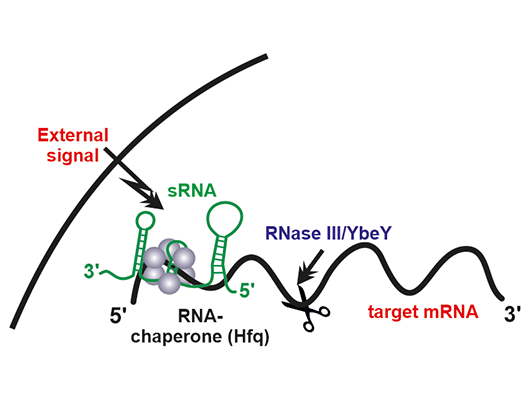
- Funstion and activity mechanisms of regulatory small non-coding RNAs
- RNA-binding proteins
Representative publications
- Beroual W, Prévost K, Lalaouna D, Ben Zaina N, Valette O, Denis Y, Djendli M, Brasseur G, Brilli M, Robledo M, Jiménez-Zurdo JI, Massé E, Biondi EG (2022) The noncoding RNA CcnA modulates the master cell cycle regulators CtrA and GcrA in Caulobacter crescentus. PLoS Biol 20: e3001528 (doi: 10.1371/journal.pbio.3001528).
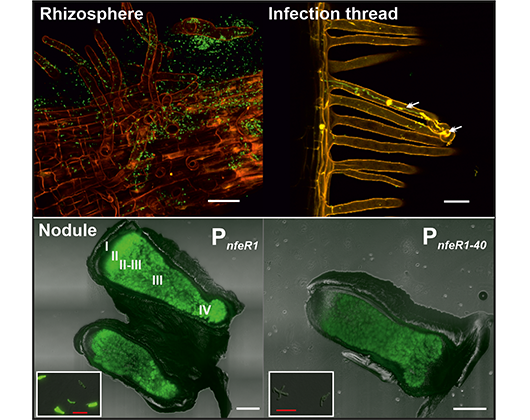
- García-Tomsig NI, Robledo M, diCenzo GC, Mengoni A, Millán V, Peregrina A, Uceta A, Jiménez-Zurdo JI (2022) Pervasive RNA regulation of metabolism enhances the root colonization ability of nitrogen-fixing symbiotic α-rhizobia. mBio 13: e0357621 (doi: 10.1128/mbio.03576-21).
- Robledo M, García-Tomsig NI, Matia-González AM, García-Rodríguez FM, Jiménez-Zurdo JI (2020) Synthetase of the methyl donor S-adenosylmethionine from nitrogen-fixing α-rhizobia can bind functionally diverse RNA species. RNA Biol 10: 1-13.
- Robledo M, García-Tomsig NI, Jiménez-Zurdo JI (2020) Riboregulation in nitrogen-fixing endosymbiotic bacteria. Microorganisms 8: 384 (doi: 10.3390/microorganisms8030384).
- Saramago M, Robledo M, Matos RG, Jiménez-Zurdo JI, Arraiano CM (2018) Sinorhizobium meliloti RNase III: catalytic features and impact on symbiosis. Front Genet 9: 350 (doi: 10.3389/fgene.2018.00350).
- Robledo M, Schlüter JP, Loehr LO, Linne U, Albaum SP, Jiménez-Zurdo JI, Becker A (2018) An sRNA and cold shock protein homolog-based feedforward loop post-transcriptionally controls cell cycle master regulator CtrA. Front Microbiol 9: 763 (doi: 10.3389/fmicb.2018.00763).
- Jiménez-Zurdo JI, Robledo M (2017) RNA silencing in plant symbiotic bacteria: Insights from a protein-centric view. RNA Biol 14: 1672-1677.
- Robledo M, Peregrina A, Millán V, García-Tomsig NI, Torres-Quesada O, Mateos PF, Becker A, Jiménez-Zurdo JI (2017) A conserved α-proteobacterial small RNA contributes to osmoadaptation and symbiotic efficiency of rhizobia on legume roots. Environ Microbiol 19: 2661-2680.
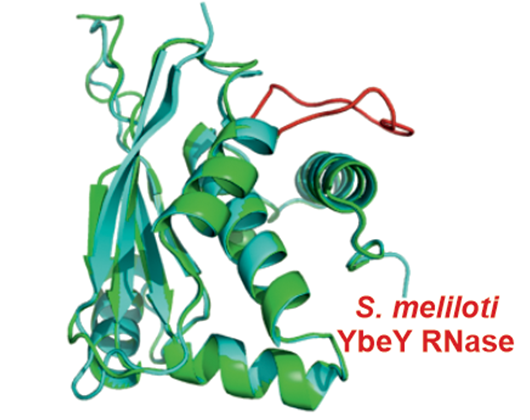
- Saramago M, Peregrina A, Robledo M, Matos RG, Hilker R, Serrania J, Becker A, Arraiano CM, Jiménez-Zurdo JI (2017) Sinorhizobium meliloti YbeY is an endoribonuclease with unprecedented catalytic features, acting as silencing enzyme in riboregulation. Nucleic Acids Res 45: 1371-1391.
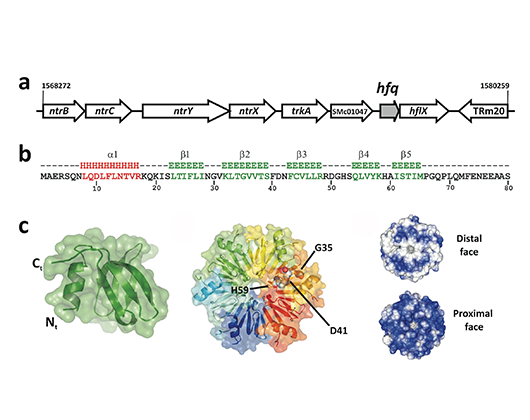
- Torres-Quesada O, Reinkensmeier J, Schlüter JP, Robledo M, Peregrina A, Giegerich R, Toro N, Becker A, Jiménez-Zurdo JI (2014) Genome-wide profiling of Hfq-binding RNAs uncovers extensive post-transcriptional rewiring of major stress response and symbiotic regulons in Sinorhizobium meliloti. RNA Biol 11: 563-579.
- Torres-Quesada O, Millán V, Nisa-Martínez R, Bardou F, Crespi M, Toro N, Jiménez-Zurdo JI (2017) Independent activity of the homologous small regulatory RNAs AbcR1 and AbcR2 in the legume symbiont Sinorhizobium meliloti. PLOS One 8: e68147 (doi: 10.1371/journal.pone.0068147).
- Jiménez-Zurdo JI, Valverde C, Becker A (2013) Insights into the noncoding RNome of nitrogen-fixing endosymbiotic α-proteobacteria. Mol Plant-Microbe Interact 26: 160-167.
- Torres-Quesada O, Oruezabal RI, Peregrina A, Jofré E, Lloret J, Rivilla R, Toro N, Jiménez-Zurdo JI (2010) The Sinorhizobium meliloti RNA chaperone Hfq influences central carbon metabolism and the symbiotic interaction with alfalfa. BMC Microbiol 10: 71 (doi: 10.1186/ 1471-2180-10-71).
- del Val C, Romero-Zaliz R, Torres-Quesada O, Peregrina A, Toro N, Jiménez-Zurdo JI (2012) A survey of sRNA families in α-proteobacteria. RNA Biol 9: 119-129.
- del Val C, Rivas E, Torres-Quesada O, Toro N, Jiménez-Zurdo JI (2007) Identification of differentially expressed small non-coding RNAs in the legume endosymbiont Sinorhizobium meliloti by comparative genomics. Mol Microbiol 66: 1080-1091.
Grants
- Jiménez Zurdo JI (IP) (2021-2024) Transcriptoma no codificante y regulación por RNA del metabolismo simbiótico en rizobios fijadores de nitrógeno. Ministerio de Ciencia e Innovación, Plan Nacional I+D+i (PID2020-114782GB-I00).
- Jiménez Zurdo JI (IP) (2021-2023) Regulación por RNA de la nodulación y fijación de nitrógeno en simbiontes de leguminosas de interés agronómico. Junta de Andalucía PAIDI/FEDER (PAIDI P20_00185).
- Jiménez Zurdo JI (co-IP) (2020-2022) Contribución del transcriptoma no codificante a la diversidad simbiótica de rizobios que nodulan leguminosas de interés agronómico. Universidad de Sevilla. FEDER US-1250546.
- Jiménez Zurdo JI (IP) (2018-2021) Mecanismos que operan en la riboregulación del metabolismo y la fijación simbiótica de nitrógeno en rizobios. Ministerio de Ciencia e Innovación. BFU2017-82645-P.
- Jiménez Zurdo JI (IP) (2014-2017) Regulación por RNAs no codificantes de la adaptación a estrés abiótico en el simbionte de leguminosas Sinorhizobium meliloti. Ministerio de Ciencia e Innovación. BFU2013-48282-C2-2-P.
- Jiménez Zurdo JI (IP) (2010-2012) Caracterización funcional de reguladores de respuesta a estrés del simbionte de alfalfa meliloti. Ministerio de Ciencia e Innovación. AGL2009-07925.
Relevant methods
• RNA-seq, dRNA-seq, Cappable-seq, Term-seq y tagRNA-seq to study structure, function, biogenesis and mechanistic principles of the bacterial non-coding transcriptome
• Bacterial molecular genetics
Collaborations with other national and international research groups
- Pedro F. Mateos (Universidad de Salamanca)
- José Mª Vinardell González (Universidad de Sevilla)
- Cecilia Arraiano (Universidade Nova de Lisboa, Portugal)
- Anke Becker (Phillips Universität Marburg, Alemania)
- Claudio Valverde (Universidad Nacional de Quilmes, Argentina)
- George C. diCenzo (Queen’s University, Canadá)
- Alessio Mengoni (Università degli Studi di Firenze, Italia)